基因数据分析软件迁移-inferCNV
【摘要】 项目说明服务器TaiShan 200服务器(型号2280)CPU鲲鹏920 5250处理器内存无要求存储无要求磁盘分区/top空间建议保留100G+网络能访问互联网操作系统Kylin Linux Advanced Server V10 (Tercel)包安装需要使用BiocManager,优先安装BiocManagerInstall.package(“BiocManager”)导入BiocM...
| 项目 | 说明 |
|---|---|
| 服务器 | TaiShan 200服务器(型号2280) |
| CPU | 鲲鹏920 5250处理器 |
| 内存 | 无要求 |
| 存储 | 无要求 |
| 磁盘分区 | /top空间建议保留100G+ |
| 网络 | 能访问互联网 |
| 操作系统 | Kylin Linux Advanced Server V10 (Tercel) |
- 包安装需要使用BiocManager,优先安装BiocManager
Install.package(“BiocManager”) - 导入BiocManager包
library(BiocManager) - 安装inferCNV
BiocManager::install("inferCNV") - 安装出现如下错误
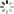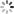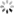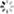
- 下载包到服务器本地,命令行安装
wget https://bioconductor.org/packages/release/bioc/src/contrib/infercnv_1.10.0.tar.gz - 命令行执行安装
R CMD INSTALL infercnv_1.10.0.tar.gz
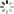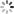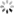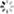
- 在rstudio console会话中使用install.packages(“包名”)安装以上依赖,若果遇到install.packages无法安装,则使用BiocManager::install(“包名”)安装
- 依赖中rjags 依赖JAGS, 步骤7方式安装会报错
- 需要安装JAGS后再返回安装rjags,下载JAGS到服务器本地
wget https://sourceforge.net/projects/mcmc-jags/files/JAGS/4.x/Source/JAGS-4.3.0.tar.gz - 解压软件包
tar -xf JAGS-4.3.0.tar.gz - 进入解压目录
cd JAGS-4.3.0/ - 执行编译
./configure --enable-shared
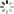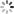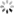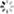
- 提示需要安装lapack
yum install -y lapack lapack-devel - 再次执行步骤12
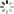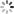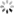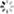
- 编译安装
make && make install - 再次执行rjags安装
Install.packages(“rjags”)
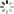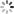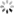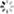
- 因为rsession是普通用户启动,权限不足,切换到linux(root用户) R命令行终端安装
- 安装完成后,回到rstudio 会话导入包
library("rjags")
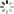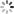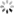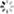
- 可以看到无法访问安装好的JAGS库,需要为rsession 登入用户(test)添加JAGS的访问权限
- 赋权后导入成功
【声明】本内容来自华为云开发者社区博主,不代表华为云及华为云开发者社区的观点和立场。转载时必须标注文章的来源(华为云社区)、文章链接、文章作者等基本信息,否则作者和本社区有权追究责任。如果您发现本社区中有涉嫌抄袭的内容,欢迎发送邮件进行举报,并提供相关证据,一经查实,本社区将立刻删除涉嫌侵权内容,举报邮箱:
cloudbbs@huaweicloud.com
- 点赞
- 收藏
- 关注作者









评论(0)